| SIRT6 |
|---|
 |
| PDBに登録されている構造 |
|---|
| PDB | オルソログ検索: RCSB PDBe PDBj |
|---|
| PDBのIDコード一覧 |
|---|
3K35, 3PKI, 3PKJ, 3ZG6 |
|
|
| 識別子 |
|---|
| 記号 | SIRT6, SIR2L6, sirtuin 6 |
|---|
| 外部ID | OMIM: 606211 MGI: 1354161 HomoloGene: 6924 GeneCards: SIRT6 |
|---|
| 遺伝子の位置 (ヒト) |
|---|
 | | 染色体 | 19番染色体 (ヒト)[1] |
|---|
| | バンド | データ無し | 開始点 | 4,174,109 bp[1] |
|---|
| 終点 | 4,182,566 bp[1] |
|---|
|
| 遺伝子の位置 (マウス) |
|---|
 | | 染色体 | 10番染色体 (マウス)[2] |
|---|
| | バンド | データ無し | 開始点 | 81,457,619 bp[2] |
|---|
| 終点 | 81,463,631 bp[2] |
|---|
|
|
| 遺伝子オントロジー |
|---|
| 分子機能 | • NAD-dependent histone deacetylase activity
• transcription corepressor activity
• protein deacetylase activity
• zinc ion binding
• クロマチン結合
• 金属イオン結合
• 血漿タンパク結合
• NAD+ ADP-ribosyltransferase activity
• 加水分解酵素活性
• NAD-dependent protein deacetylase activity
• NAD+ binding
• NAD+-protein-arginine ADP-ribosyltransferase activity
• NAD-dependent histone deacetylase activity (H3-K9 specific)
• histone deacetylase activity
|
|---|
| 細胞の構成要素 | • 細胞質
• 核小体
• 核質
• 細胞核
|
|---|
| 生物学的プロセス | • negative regulation of glycolytic process
• glucose homeostasis
• regulation of double-strand break repair via homologous recombination
• positive regulation of fibroblast proliferation
• protein deacetylation
• negative regulation of glucose import
• response to nutrient levels
• protein destabilization
• post-embryonic cardiac muscle cell growth involved in heart morphogenesis
• negative regulation of transcription, DNA-templated
• positive regulation of stem cell proliferation
• base-excision repair
• negative regulation of cell population proliferation
• histone deacetylation
• histone H3-K9 modification
• histone H3-K9 deacetylation
• protein ADP-ribosylation
• positive regulation of telomere maintenance
• positive regulation of chondrocyte proliferation
• positive regulation of blood vessel branching
• positive regulation of vascular endothelial cell proliferation
• positive regulation of cold-induced thermogenesis
• negative regulation of transcription by RNA polymerase II
• histone H3 deacetylation
|
|---|
| 出典:Amigo / QuickGO |
|
| オルソログ |
|---|
| 種 | ヒト | マウス |
|---|
| Entrez | | |
|---|
| Ensembl | | |
|---|
| UniProt | | |
|---|
RefSeq
(mRNA) | NM_001193285
NM_016539
NM_001321058
NM_001321059
NM_001321060
|
|---|
NM_001321061
NM_001321062
NM_001321063
NM_001321064 |
| |
|---|
NM_001163430
NM_181586
NM_001378944
NM_001378945 |
|
|---|
RefSeq
(タンパク質) | NP_001180214
NP_001307987
NP_001307988
NP_001307989
NP_001307990
|
|---|
NP_001307991
NP_001307992
NP_001307993
NP_057623 |
| |
|---|
NP_001156902
NP_853617
NP_001365873
NP_001365874 |
|
|---|
場所
(UCSC) | Chr 19: 4.17 – 4.18 Mb | Chr 19: 81.46 – 81.46 Mb |
|---|
| PubMed検索 | [3] | [4] |
|---|
| ウィキデータ |
|
サーチュイン6(英: sirtuin 6、SIRT6)は、ストレス応答性のタンパク質脱アセチル化酵素・モノADPリボシル化酵素であり、ヒトではSIRT6遺伝子にコードされる[5][6][7]。DNA修復、テロメアの維持、解糖系、炎症など、老化と関連した複数の経路で機能していることが実験室レベルでの研究から示唆されている[5]。SIRT6はサーチュインファミリーのメンバーであり、酵母のSir2タンパク質と相同である。
研究
SIRT6はヒストンH3とH4に対する脱アセチル化酵素(デアセチラーゼ)であり、クロマチンの密度を変化させて遺伝子発現を調節する活性が持つことが主に知られている。サーチュインファミリーの他のメンバーと同様、SIRT6の酵素活性は補因子であるニコチンアミドアデニンジヌクレオチド(NAD+)の結合に依存している[8]。
Sirt6を過剰発現するよう遺伝子改変されたマウスでは、最長寿命の伸長がみられる。寿命の伸長効果は約15–16%であり、オスのマウスでのみ観察される[9]。
DNA修復
SIRT6はクロマチン結合タンパク質であり、哺乳類細胞においてDNA損傷に対する正常な塩基除去修復や二本鎖切断修復に必要とされる[10][11]。Sirt6が欠乏したマウスでは、老化と関係した変性過程と重複する異常が観察される[10]。18種の齧歯類に対する研究では、その種の寿命とSirt6酵素の効率との相関関係が示されている[11]。
SIRT6は非相同末端結合や相同組換え過程によってDNA二本鎖切断の修復を促進する[12]。SIRT6はクロマチンの損傷部位で修復タンパク質DNA-PKcsを安定化する[13]。
正常なヒト線維芽細胞では、複製を行うことで複製老化へ進行するにつれて相同組換え修復の能力は低下する[14]。しかしながら、middle-aged(PD52–53)やpre-senescent(PD60–62)状態の細胞でのSIRT6の過剰発現は、相同組換え修復を強力に刺激する[14]。この効果はPARP1に対するモノADPリボシル化活性に依存している。SIRT6は老化ヒト線維芽細胞での塩基除去修復もPARP1依存的に回復する[15]。
活性化剤
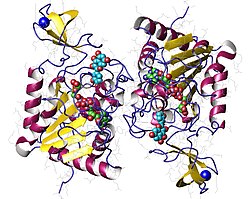
SIRT6の脱アセチル化活性は高濃度(数百μM)の脂肪酸によって[16]、そしてピロロ[1,2-a]キノキサリン骨格を持つ合成活性化剤によってより強力に刺激される[17]。SIRT6/活性化剤複合体の結晶構造からは、化合物が酵素のアシル基結合チャネルのSIRT6特異的ポケットを利用していることが示されている[17]。研究されている多くのアントシアニジンの中では、シアニジンが最も強力にSIRT6の活性を刺激する[12]。
出典
- ^ a b c GRCh38: Ensembl release 89: ENSG00000077463 - Ensembl, May 2017
- ^ a b c GRCm38: Ensembl release 89: ENSMUSG00000034748 - Ensembl, May 2017
- ^ Human PubMed Reference:
- ^ Mouse PubMed Reference:
- ^ a b “Phylogenetic classification of prokaryotic and eukaryotic Sir2-like proteins”. Biochemical and Biophysical Research Communications 273 (2): 793–98. (July 2000). doi:10.1006/bbrc.2000.3000. PMID 10873683.
- ^ “Entrez Gene: SIRT6 sirtuin (silent mating type information regulation 2 homolog) 6 (S. cerevisiae)”. 2022年5月6日閲覧。
- ^ “Repairing split ends: SIRT6, mono-ADP ribosylation and DNA repair”. Aging 3 (9): 829–835. (2011). doi:10.18632/aging.100389. PMC 3227448. PMID 21946623. https://www.jbc.org/content/295/32/11021.long.
- ^ “Slowing ageing by design: the rise of NAD + and sirtuin-activating compounds”. Nat Rev Mol Cell Biol 17 (11): 679–690. (2016). doi:10.1038/nrm.2016.93. PMC 5107309. PMID 27552971. https://www.ncbi.nlm.nih.gov/pmc/articles/PMC5107309/.
- ^ “The sirtuin SIRT6 regulates lifespan in male mice”. Nature 483 (7388): 218–21. (February 2012). Bibcode: 2012Natur.483..218K. doi:10.1038/nature10815. PMID 22367546.
- ^ a b “Genomic instability and aging-like phenotype in the absence of mammalian SIRT6”. Cell 124 (2): 315–29. (January 2006). doi:10.1016/j.cell.2005.11.044. PMID 16439206.
- ^ a b “SIRT6 Is Responsible for More Efficient DNA Double-Strand Break Repair in Long-Lived Species”. Cell 177 (3): 622–638. (2019). doi:10.1016/j.cell.2019.03.043. PMC 6499390. PMID 31002797. https://www.jbc.org/content/295/32/11021.long.
- ^ a b “Biological and catalytic functions of sirtuin 6 as targets for small-molecule modulators”. Journal of Biological Chemistry 295 (32): 11021–11041. (2020). doi:10.1074/jbc.REV120.011438. PMC 7415977. PMID 32518153. https://www.jbc.org/content/295/32/11021.long.
- ^ “SIRT6 stabilizes DNA-dependent protein kinase at chromatin for DNA double-strand break repair”. Aging 1 (1): 109–21. (January 2009). doi:10.18632/aging.100011. PMC 2815768. PMID 20157594. https://www.ncbi.nlm.nih.gov/pmc/articles/PMC2815768/.
- ^ a b “Sirtuin 6 (SIRT6) rescues the decline of homologous recombination repair during replicative senescence”. Proceedings of the National Academy of Sciences of the United States of America 109 (29): 11800–05. (July 2012). Bibcode: 2012PNAS..10911800M. doi:10.1073/pnas.1200583109. PMC 3406824. PMID 22753495. https://www.ncbi.nlm.nih.gov/pmc/articles/PMC3406824/.
- ^ “SIRT6 rescues the age related decline in base excision repair in a PARP1-dependent manner”. Cell Cycle 14 (2): 269–76. (2015). doi:10.4161/15384101.2014.980641. PMC 4614943. PMID 25607651. https://www.ncbi.nlm.nih.gov/pmc/articles/PMC4614943/.
- ^ “Activation of the protein deacetylase SIRT6 by long-chain fatty acids and widespread deacylation by mammalian sirtuins”. The Journal of Biological Chemistry 288 (43): 31350–56. (October 2013). doi:10.1074/jbc.C113.511261. PMC 3829447. PMID 24052263. https://www.ncbi.nlm.nih.gov/pmc/articles/PMC3829447/.
- ^ a b “Structural Basis of Sirtuin 6 Activation by Synthetic Small Molecules”. Angewandte Chemie 56 (4): 1007–11. (January 2017). doi:10.1002/anie.201610082. PMID 27990725.
外部リンク
- FactorBook SIRT6
- Overview of all the structural information available in the PDB for UniProt: Q8N6T7 (NAD-dependent protein deacetylase sirtuin-6) at the PDBe-KB.